Molekulare Modelle der DNA - Molecular models of DNA
Molekülmodelle von DNA-Strukturen sind Darstellungen der molekularen Geometrie und Topologie von Desoxyribonukleinsäure ( DNA )-Molekülen mit einem von mehreren Mitteln mit dem Ziel, die wesentlichen, physikalischen und chemischen Eigenschaften von DNA-Molekülstrukturen entweder in vivo oder in zu vereinfachen und darzustellen Vitro . Diese Darstellungen umfassen dicht gepackte Kugeln ( CPK- Modelle) aus Kunststoff, Metalldrähte für Skelettmodelle , grafische Berechnungen und Animationen durch Computer, künstlerisches Rendering. Molekulare Computermodelle ermöglichen auch Animationen und Molekulardynamiksimulationen, die für das Verständnis der DNA-Funktion in vivo sehr wichtig sind .
Die fortgeschritteneren, computerbasierten Molekülmodelle der DNA beinhalten molekulardynamische Simulationen und quantenmechanische Berechnungen von Vibrationsrotationen, delokalisierten Molekülorbitalen (MOs), elektrischen Dipolmomenten , Wasserstoffbrückenbindungen und so weiter. Die DNA-Molekulardynamik-Modellierung beinhaltet die Simulation von molekularen Geometrie- und Topologieänderungen von Desoxyribonukleinsäure ( DNA ) mit der Zeit als Ergebnis sowohl intra- als auch intermolekularer Wechselwirkungen der DNA. Während molekulare Modelle von DNA-Molekülen wie dicht gepackte Kugeln (CPK-Modelle) aus Kunststoff- oder Metalldrähten für Skelettmodelle brauchbare Darstellungen statischer DNA-Strukturen sind, ist ihre Brauchbarkeit zur Darstellung komplexer DNA-Dynamik sehr begrenzt. Die computergestützte Molekularmodellierung ermöglicht sowohl Animationen als auch molekulare Dynamiksimulationen, die sehr wichtig sind, um zu verstehen, wie DNA in vivo funktioniert .
Geschichte
Bereits in den frühen Stadien der Strukturuntersuchungen von DNA durch Röntgenbeugung und biochemische Mittel wurden molekulare Modelle wie das Nukleinsäure-Doppelhelix- Modell von Watson-Crick erfolgreich eingesetzt, um das "Rätsel" der DNA-Struktur zu lösen und auch herauszufinden, wie die letzteres bezieht sich auf seine Schlüsselfunktionen in lebenden Zellen. Die ersten hochwertigen Röntgenbeugungsmuster von A-DNA wurden 1953 von Rosalind Franklin und Raymond Gosling beschrieben . Rosalind Franklin machte die kritische Beobachtung, dass DNA in zwei unterschiedlichen Formen existiert, A und B, und produzierte die schärfsten Bilder von beiden durch Röntgenbeugungstechnik. Die ersten Berechnungen der Fourier-Transformation einer atomaren Helix wurden ein Jahr zuvor von Cochran, Crick und Vand beschrieben, und 1953 folgte die Berechnung der Fourier-Transformation einer Coiled-Coil von Crick.
Strukturelle Informationen werden aus Röntgenbeugungsuntersuchungen orientierter DNA-Fasern mit Hilfe von molekularen DNA-Modellen generiert, die mit kristallographischer und mathematischer Analyse der Röntgenmuster kombiniert werden.
Die ersten Berichte über ein Doppelhelix-Molekülmodell der B-DNA-Struktur wurden 1953 von James Watson und Francis Crick gemacht. Im selben Jahr berichteten Maurice F. Wilkins, A. Stokes und HR Wilson über die ersten Röntgenmuster von in vivo B-DNA in teilweise orientierten Lachsspermienköpfen.
Die Entwicklung des ersten korrekten Doppelhelix-Molekülmodells der DNA durch Crick und Watson wäre ohne den biochemischen Nachweis der Nukleotidbasenpaarung ([A---T]; [C---G]) möglicherweise nicht möglich gewesen, oder Chargaffs Regeln . Obwohl solche anfänglichen Untersuchungen von DNA-Strukturen mit Hilfe molekularer Modelle im Wesentlichen statisch waren, waren ihre Konsequenzen für die Erklärung der in-vivo- Funktionen der DNA auf den Gebieten der Proteinbiosynthese und der Quasi-Universalität des genetischen Codes bedeutsam. Epigenetische Transformationsstudien von DNA in vivo entwickelten sich jedoch trotz ihrer Bedeutung für die Embryologie, Morphogenese und Krebsforschung viel langsamer. Solche chemischen Dynamiken und biochemischen Reaktionen der DNA sind viel komplexer als die molekularen Dynamiken der physikalischen DNA-Wechselwirkungen mit Wasser, Ionen und Proteinen/Enzymen in lebenden Zellen.
Bedeutung
Ein altes dynamisches Problem besteht darin, wie die DNA-"Selbstreplikation" in lebenden Zellen stattfindet, die ein vorübergehendes Abwickeln von superspiralisierten DNA-Fasern beinhalten sollte. Obwohl die DNA aus relativ starren, sehr großen verlängerten Biopolymermolekülen besteht, die als Fasern oder Ketten bezeichnet werden (die aus sich wiederholenden Nukleotideinheiten von vier Grundtypen bestehen, die an Desoxyribose- und Phosphatgruppen befestigt sind), unterliegt ihre Molekülstruktur in vivo dynamischen Konfigurationsänderungen, die dynamisch verbunden sind Wassermoleküle und Ionen. Supercoiling, Packen mit Histonen in Chromosomenstrukturen und andere derartige supramolekulare Aspekte beinhalten auch die in vivo- DNA-Topologie, die noch komplexer ist als die DNA-Molekülgeometrie, was die molekulare Modellierung von DNA sowohl für Molekularbiologen als auch Biotechnologen zu einem besonders herausfordernden Problem macht. Wie andere große Moleküle und Biopolymere existiert DNA oft in mehreren stabilen Geometrien (d. h. sie weist Konformationsisomerie auf ) und konfigurativen Quantenzuständen, die auf der potentiellen Energieoberfläche des DNA-Moleküls energetisch nahe beieinander liegen.
Solche unterschiedlichen Molekülgeometrien können zumindest im Prinzip auch berechnet werden, indem man ab-initio- Quantenchemie- Methoden verwendet, die eine hohe Genauigkeit für kleine Moleküle erreichen können, obwohl kürzlich behauptet wurde, dass eine akzeptable Genauigkeit auch für Polynukleotide und DNA-Konformationen erreicht werden kann die Basis von Schwingungszirkulardichroismus (VCD) Spektraldaten. Solche Quantengeometrien definieren eine wichtige Klasse von molekularen Ab-initio- Modellen der DNA, deren Erforschung gerade erst begonnen hat, insbesondere in Bezug auf Ergebnisse, die durch VCD in Lösungen erhalten wurden. Detailliertere Vergleiche mit solchen Ab-initio- Quantenrechnungen sind prinzipiell durch 2D-FT-NMR-Spektroskopie und Relaxationsstudien von Polynukleotidlösungen oder spezifisch markierter DNA, wie beispielsweise mit Deuteriummarkern, möglich.
In einem interessanten Rollenwechsel wurde vorgeschlagen, dass das DNA-Molekül für Quantencomputer über DNA verwendet wird. Es wurden sowohl DNA-Nanostrukturen als auch DNA-Computing- Biochips gebaut.
Grundsätzliche Konzepte
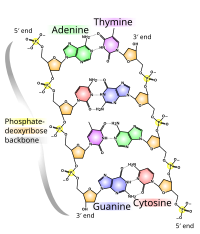
Die chemische Struktur der DNA reicht nicht aus, um die Komplexität der 3D-Strukturen der DNA zu verstehen. Im Gegensatz dazu ermöglichen animierte Molekülmodelle die visuelle Untersuchung der dreidimensionalen (3D) Struktur der DNA. Das gezeigte DNA-Modell (ganz rechts) ist ein raumfüllendes oder CPK- Modell der DNA-Doppelhelix. Animierte molekulare Modelle, wie der Draht- oder Skeletttyp, der oben in diesem Artikel gezeigt wird, ermöglichen es, die dreidimensionale (3D) Struktur der DNA visuell zu erkunden. Eine andere Art von DNA-Modell ist das raumfüllende oder CPK-Modell.
Die Dynamik der Wasserstoffbrückenbindung und der Protonenaustausch unterscheiden sich zwischen den beiden Systemen aus vollständig hydratisierter DNA und Wassermolekülen im Eis um viele Größenordnungen. Daher ist die DNA-Dynamik komplex und umfasst Nanosekunden- und mehrere zehn Pikosekunden-Zeitskalen, während die von flüssigem Eis auf der Pikosekunden-Zeitskala liegt und die des Protonenaustauschs in Eis auf der Millisekunden-Zeitskala liegt. Die Protonenaustauschraten in DNA und angelagerten Proteinen können von Pikosekunden bis Nanosekunden, Minuten oder Jahren variieren, abhängig von der genauen Position der ausgetauschten Protonen in den großen Biopolymeren.
Eine einfache harmonische Oszillator- "Schwingung" ist nur eine stark vereinfachte dynamische Darstellung der longitudinalen Schwingungen der DNA-verflochtenen Helices, die sich als anharmonisch statt harmonisch erwiesen haben, wie oft in quantendynamischen Simulationen von DNA angenommen.
DNA-Struktur
Die Struktur der DNA zeigt eine Vielzahl von Formen, sowohl doppelsträngig als auch einzelsträngig. Die mechanischen Eigenschaften der DNA, die in direktem Zusammenhang mit ihrer Struktur stehen, stellen für Zellen ein erhebliches Problem dar . Jeder Prozess, der DNA bindet oder liest, ist in der Lage, die mechanischen Eigenschaften der DNA zum Zwecke der Erkennung, Verpackung und Modifikation zu nutzen oder zu modifizieren. Die extreme Länge (ein Chromosom kann einen 10 cm langen DNA-Strang enthalten), die relative Starrheit und die helikale Struktur der DNA haben zur Entwicklung von Histonen und von Enzymen wie Topoisomerasen und Helikasen geführt , um die DNA einer Zelle zu verwalten. Die Eigenschaften der DNA hängen eng mit ihrer molekularen Struktur und Sequenz zusammen, insbesondere mit der Schwäche der Wasserstoffbrückenbindungen und elektronischen Wechselwirkungen, die DNA-Stränge zusammenhalten, verglichen mit der Stärke der Bindungen innerhalb jedes Strangs.
Experimentelle Methoden, mit denen die mechanischen Eigenschaften von DNA direkt gemessen werden können, sind relativ neu, und eine hochauflösende Visualisierung in Lösung ist oft schwierig. Dennoch haben Wissenschaftler große Datenmengen zu den mechanischen Eigenschaften dieses Polymers aufgedeckt, und die Auswirkungen der mechanischen Eigenschaften der DNA auf zelluläre Prozesse sind Gegenstand aktueller Forschung.
Die in vielen Zellen gefundene DNA kann eine makroskopisch lange Länge haben: einige Zentimeter für jedes menschliche Chromosom. Folglich müssen Zellen DNA verdichten oder verpacken , um sie in sich zu tragen. In Eukaryoten wird dies von spulenartigen Proteinen namens Histone getragen , um die sich die DNA windet. Es ist die weitere Verdichtung dieses DNA-Protein-Komplexes, die die bekannten mitotischen eukaryotischen Chromosomen produziert .
In den späten 1970er Jahren wurden alternative nicht-helikale Modelle der DNA-Struktur kurz als mögliche Lösung für Probleme bei der DNA-Replikation in Plasmiden und Chromatin betrachtet . Die Modelle wurden jedoch aufgrund späterer experimenteller Fortschritte wie der Röntgenkristallographie von DNA-Duplexen und später des Nukleosom-Kernpartikels und der Entdeckung von Topoisomerasen zugunsten des Doppelhelix-Modells verworfen . Solche nicht-doppelhelikalen Modelle werden derzeit von der Mainstream-Wissenschaftsgemeinschaft nicht akzeptiert.
DNA-Strukturbestimmung mit Molecular Modeling und DNA-Röntgenmustern
Nachdem die DNA durch biochemische Standardmethoden getrennt und gereinigt wurde, hat man eine Probe in einem Gefäß, ähnlich wie in der Abbildung oben in diesem Artikel. Im Folgenden sind die wichtigsten Schritte aufgeführt, die bei der Generierung von Strukturinformationen aus Röntgenbeugungsstudien orientierter DNA-Fasern, die aus der hydratisierten DNA-Probe mit Hilfe von molekularen DNA-Modellen gezogen werden, die mit kristallographischer und mathematischer Analyse der Röntgenmuster kombiniert werden, erforderlich sind .
Parakristalline Gittermodelle von B-DNA-Strukturen

Ein parakristallines Gitter oder Parakristall ist ein molekulares oder atomares Gitter mit signifikanten Mengen (z. B. größer als ein paar Prozent) an teilweiser Unordnung molekularer Anordnungen. Grenzfälle des Parakristallmodells sind Nanostrukturen , wie Gläser , Flüssigkeiten usw., die möglicherweise nur eine lokale und keine globale Ordnung besitzen. Ein einfaches Beispiel für ein parakristallines Gitter ist in der folgenden Abbildung für ein Quarzglas dargestellt:
Flüssigkristalle haben auch eher parakristalline als kristalline Strukturen.
Hochhydratisierte B-DNA kommt natürlicherweise in lebenden Zellen in einem solchen parakristallinen Zustand vor, der trotz der relativ starren DNA-Doppelhelix, die durch parallele Wasserstoffbrücken zwischen den Nukleotidbasenpaaren in den beiden komplementären, helikalen DNA-Ketten stabilisiert wird, dynamisch ist (siehe Abbildungen). ). Der Einfachheit halber lassen die meisten DNA-Molekülmodelle sowohl Wasser als auch dynamisch an B-DNA gebundene Ionen weg und sind daher für das Verständnis des dynamischen Verhaltens von B-DNA in vivo weniger nützlich . Die physikalische und mathematische Analyse von Röntgen- und spektroskopischen Daten für parakristalline B-DNA ist daher weitaus komplexer als die von kristallinen A-DNA-Röntgenbeugungsmustern. Das Parakristallmodell ist auch für DNA-technische Anwendungen wie die DNA-Nanotechnologie wichtig . Inzwischen werden auch neue Verfahren entwickelt, die die Röntgenbeugung von DNA mit der Röntgenmikroskopie in hydratisierten lebenden Zellen kombinieren.
Genomische und biotechnologische Anwendungen der DNA-Molekularmodellierung

Es gibt verschiedene Anwendungen des DNA-Molekularmodellings in Forschungsanwendungen in Genomik und Biotechnologie, von DNA-Reparatur bis hin zu PCR und DNA-Nanostrukturen . Zweidimensionale DNA-Junction-Arrays wurden durch Rasterkraftmikroskopie sichtbar gemacht .
DNA-Molekularmodellierung hat verschiedene Anwendungen in der Genomik und Biotechnologie , wobei die Forschungsanwendungen von DNA-Reparatur bis hin zu PCR und DNA-Nanostrukturen reichen. Dazu gehören molekulare Computermodelle von so unterschiedlichen Molekülen wie RNA-Polymerase, ein E. coli, bakterielles DNA-Primase-Templat, das auf eine sehr komplexe Dynamik an den Grenzflächen zwischen den Enzymen und dem DNA-Templat hindeutet, und molekulare Modelle der mutagenen, chemischen Wechselwirkung potenter krebserregender Moleküle mit DNA. Diese sind alle in der Galerie unten dargestellt.
Zu den technologischen Anwendungen gehören ein DNA-Biochip und DNA-Nanostrukturen, die für DNA-Computing und andere dynamische Anwendungen der DNA-Nanotechnologie entwickelt wurden . Das Bild rechts zeigt selbstorganisierte DNA-Nanostrukturen. Die DNA-"Kachel"-Struktur in diesem Bild besteht aus vier verzweigten Verbindungen, die in einem Winkel von 90° orientiert sind. Jede Kachel besteht wie gezeigt aus neun DNA-Oligonukleotiden; solche Kacheln dienen als primärer „Baustein“ für den Zusammenbau der DNA-Nanogitter, die in der AFM-Aufnahme gezeigt werden.
Quadruplex-DNA kann an bestimmten Krebsarten beteiligt sein. Bilder von Quadruplex-DNA finden Sie in der Galerie unten.
Galerie der DNA-Modelle
15 m langes DNA-Modell, Naturalis Biodiversity Center
Siehe auch
- G-Quadruplex
- Kristallographie
- Kristallgitter
- Dinukleotid-Eigenschaftsdatenbank ( DiProDB ), die entwickelt wurde, um thermodynamische, strukturelle und andere Dinukleotid-Merkmale zu sammeln und zu analysieren
- Röntgenmikroskopie
- Röntgenstreuung
- Neutronenstreuung
- Nukleinsäuresequenz
- Schwingungszirkulardichroismus (VCD)
- Raman-Spektroskopie -Mikroskopie und kohärente Anti-Stokes-Raman-Spektroskopie (CARS)
- Sir Lawrence Bragg , FRS
- Vergleich von Nukleinsäure-Simulationssoftware
- BERNSTEIN
- CHARMM
- Abalone (Molekularmechanik)
- Visualisierungssoftware Sirius
- QMC@Home
- NMR-Spektroskopie (FT-NMR)
- NMR - Bildgebungsmikroskopie
- Mikrowellenspektroskopie
- FT- Infrarot (IR)
- FT- Nahinfrarotspektroskopie (NIR)
- Spektrale Bildgebung , Hyperspektrale Bildgebung , chemische Bildgebung
- Fluoreszenzkorrelationsspektroskopie
- Fluoreszenz-Kreuzkorrelationsspektroskopie und Förster-Resonanz-Energietransfer (FRET)
- Konfokale Mikroskopie
- Veraltete Modelle der DNA-Struktur
Verweise
Weiterlesen
- Anwendungen neuartiger Techniken auf Reformkost, medizinische und landwirtschaftliche Biotechnologie . (Juni 2004) IC Bainu, PR Lozano, VI Prisecaru und HC Lin., q-bio/0406047.
- F. Bessel, Untersuchung des Theils der planetarischen Störungen , Berliner Abhandlungen (1824), Artikel 14.
- Sir Lawrence Bragg, FRS. Der kristalline Zustand, eine allgemeine Übersicht. London: G. Bells and Sons, Ltd., Bd. 1 und 2., 1966., 2024 Seiten.
- Cantor, CR und Schimmel, PR Biophysical Chemistry, Teil I und II ., San Francisco: WH Freeman und Co. 1980. 1800 Seiten.
- Voet, D. und JG Voet. Biochemistry , 2. Aufl., New York, Toronto, Singapur: John Wiley & Sons, Inc., 1995, ISBN 0-471-58651-X ., 1361 Seiten.
- Watson, GN Eine Abhandlung über die Theorie der Bessel-Funktionen ., (1995) Cambridge University Press. ISBN 0-521-48391-3 .
- Watson, James D. Molekularbiologie des Gens. New York und Amsterdam: WA Benjamin, Inc. 1965, 494 Seiten.
- Wentworth, WE Physikalische Chemie. Ein kurzer Kurs. , Malden (Massa.): Blackwell Science, Inc. 2000.
- Herbert R. Wilson, FRS. Beugung von Röntgenstrahlen durch Proteine, Nukleinsäuren und Viren ., London: Edward Arnold (Publishers) Ltd. 1966.
- Kurt Wüthrich. NMR von Proteinen und Nukleinsäuren. , New York, Brisbane, Chicago, Toronto, Singapur: J. Wiley & Sons. 1986., 292 Seiten.
- Hallin PF, David Ussery D (2004). "CBS Genome Atlas Database: Ein dynamischer Speicher für bioinformatische Ergebnisse und DNA-Sequenzdaten" . Bioinformatik . 20 (18): 3682–6. doi : 10.1093/bioinformatics/bth423 . PMID 15256401 .
- Zhang CT, Zhang R, Ou HY (2003). "Die Z-Kurven-Datenbank: eine grafische Darstellung von Genomsequenzen" . Bioinformatik . 19 (5): 593–599. doi : 10.1093/bioinformatics/btg041 . PMID 12651717 .
Externe Links
- DNA the Double Helix Game Von der offiziellen Nobelpreis-Website
- MDDNA: Strukturelle Bioinformatik der DNA
- Doppelhelix 1953–2003 National Center for Biotechnology Education
- DNAlive: eine Webschnittstelle zur Berechnung der physikalischen Eigenschaften von DNA . Ermöglicht auch die Vernetzung der Ergebnisse mit dem UCSC Genome Browser und DNA Dynamics.
- Weitere Details zur mathematischen und molekularen Analyse der DNA-Struktur anhand von Röntgendaten
- Bessel-Funktionen, die Fourier-Transformationen von atomaren oder molekularen Helices entsprechen.
- Überblick über STM/AFM/SNOM-Prinzipien mit Lehrvideos
Datenbanken für DNA-Molekülmodelle und -Sequenzen
- Röntgenbeugung
- NDB-ID: UD0017 Datenbank
- Röntgenatlas -Datenbank
- PDB-Dateien mit Koordinaten für Nukleinsäurestrukturen aus Röntgenbeugung durch NA-Kristalle (inkl. DNA)
- Strukturfaktoren herunterladbare Dateien im CIF-Format
- Neutronenstreuung
- ISIS-Neutronenquelle : ISIS-gepulste Neutronenquelle: Ein Weltzentrum für Wissenschaft mit Neutronen und Myonen in Harwell, in der Nähe von Oxford, Großbritannien.
- Röntgenmikroskopie
- Elektronenmikroskopie
- NMR-Datenbanken
- NMR Atlas--Datenbank-
- mmcif herunterladbare Koordinatendateien von Nukleinsäuren in Lösung aus 2D-FT-NMR-Daten
- NMR-Constraint-Dateien für NAs im PDB-Format
- Genomische und strukturelle Datenbanken
- CBS Genome Atlas Database — enthält Beispiele für Basisverzerrungen.
- Die Z-Kurvendatenbank der Genome – ein dreidimensionales Visualisierungs- und Analysewerkzeug von Genomen .
- Molekülmodelle von DNA und anderen Nukleinsäuren: Koordinatendateien von Molekülstrukturmodellen von Nukleinsäuren im PDB- und CIF-Format
- Rasterkraftmikroskopie