Phylogenetischer Baum - Phylogenetic tree
| Teil einer Serie über |
| Evolutionsbiologie |
|---|
|

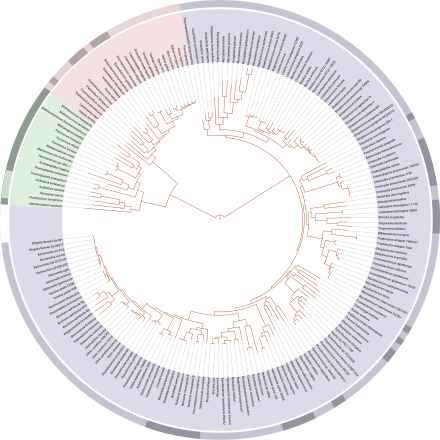
Ein phylogenetischer Baum (auch Phylogenie oder Evolutionsbaum ) ist ein verzweigtes Diagramm oder ein Baum , der die evolutionären Beziehungen zwischen verschiedenen biologischen Arten oder anderen Entitäten basierend auf Ähnlichkeiten und Unterschieden in ihren physischen oder genetischen Eigenschaften zeigt. Alles Leben auf der Erde ist Teil eines einzigen phylogenetischen Baumes, der auf eine gemeinsame Abstammung hinweist .
In einem verwurzelten phylogenetischen Baum repräsentiert jeder Knoten mit Nachkommen den abgeleiteten jüngsten gemeinsamen Vorfahren dieser Nachkommen, und die Kantenlängen in einigen Bäumen können als Zeitschätzungen interpretiert werden. Jeder Knoten wird als taxonomische Einheit bezeichnet. Interne Knoten werden im Allgemeinen als hypothetische taxonomische Einheiten bezeichnet, da sie nicht direkt beobachtet werden können. Bäume sind in Bereichen der Biologie wie Bioinformatik , Systematik und Phylogenetik nützlich . Unbewurzelte Bäume veranschaulichen nur die Verwandtschaft der Blattknoten und erfordern nicht, dass die Stammwurzel bekannt oder abgeleitet wird.
Geschichte
Die Idee eines „ Baums des Lebens “ entstand aus alten Vorstellungen eines leiterartigen Fortschreitens von niederen in höhere Lebensformen (wie in der Großen Kette des Seins ). Frühe Darstellungen von "verzweigenden" phylogenetischen Bäumen umfassen eine "paläontologische Karte", die die geologischen Beziehungen zwischen Pflanzen und Tieren im Buch Elementary Geology von Edward Hitchcock (Erstausgabe: 1840) zeigt.
Charles Darwin (1859) produzierte auch eine der ersten Illustrationen und machte in seinem bahnbrechenden Buch The Origin of Species den Begriff eines evolutionären "Baums" entscheidend populär . Mehr als ein Jahrhundert später verwenden Evolutionsbiologen immer noch Baumdiagramme , um die Evolution darzustellen, da solche Diagramme effektiv das Konzept vermitteln, dass die Artbildung durch die adaptive und halbzufällige Aufspaltung von Abstammungslinien erfolgt. Im Laufe der Zeit ist die Artenklassifizierung weniger statisch und dynamischer geworden.
Der Begriff phylogenetischen oder Phylogenie , ergibt sich aus den beiden antiken griechischen Wörter φῦλον ( phûlon ), was bedeutet , „Rasse, Abstammung“ und γένεσις ( génesis ), was bedeutet „Ursprung, Herkunft“.
Eigenschaften
Verwurzelter Baum

Ein verwurzelter phylogenetischer Baum (siehe zwei Grafiken oben) ist ein gerichteter Baum mit einem einzigartigen Knoten – der Wurzel –, der dem (normalerweise unterstellten ) jüngsten gemeinsamen Vorfahren aller Entitäten an den Blättern des Baumes entspricht. Der Wurzelknoten hat keinen übergeordneten Knoten, dient aber als übergeordneter Knoten aller anderen Knoten im Baum. Die Wurzel ist daher ein Knoten vom Grad 2, während andere interne Knoten einen minimalen Grad von 3 haben (wobei "Grad" sich hier auf die Gesamtzahl der ein- und ausgehenden Kanten bezieht).
Die gebräuchlichste Methode zum Wurzeln von Bäumen ist die Verwendung einer unumstrittenen Fremdgruppe – nahe genug, um Rückschlüsse aus Merkmalsdaten oder molekularer Sequenzierung zu ermöglichen, aber weit genug, um eine klare Fremdgruppe zu sein.
Entwurzelter Baum
Unbewurzelte Bäume veranschaulichen die Verwandtschaft der Blattknoten, ohne Annahmen über die Abstammung zu treffen. Sie erfordern nicht, dass die Stammwurzel bekannt oder abgeleitet wird. Unbewurzelte Bäume können immer aus bewurzelten erzeugt werden, indem einfach die Wurzel weggelassen wird. Im Gegensatz dazu erfordert das Ableiten der Wurzel eines nicht verwurzelten Baumes einige Mittel zur Identifizierung der Abstammung. Dies geschieht normalerweise, indem eine Fremdgruppe in die Eingabedaten aufgenommen wird, sodass die Wurzel notwendigerweise zwischen der Fremdgruppe und dem Rest der Taxa im Baum liegt, oder indem zusätzliche Annahmen über die relativen Evolutionsraten für jeden Zweig eingeführt werden, z. B. eine Anwendung der Hypothese der molekularen Uhr .
Bifurcating versus multifurcating
Sowohl bewurzelte als auch unbewurzelte Bäume können entweder gegabelt oder mehrfurkig sein. Ein verwurzelter gabelförmiger Baum hat genau zwei Nachkommen, die von jedem inneren Knoten abstammen (das heißt, er bildet einen binären Baum ), und ein unverwurzelter gabelförmiger Baum nimmt die Form eines nicht verwurzelten binären Baums an , ein freier Baum mit genau drei Nachbarn an jedem inneren Knoten. Im Gegensatz dazu kann ein verwurzelter mehrverzweigter Baum mehr als zwei Kinder an einigen Knoten haben und ein unverwurzelter mehrverzweigter Baum kann an einigen Knoten mehr als drei Nachbarn haben.
Beschriftet versus unbeschriftet
Sowohl bewurzelte als auch unbewurzelte Bäume können entweder beschriftet oder unbeschriftet sein. Einem beschrifteten Baum sind seinen Blättern bestimmte Werte zugewiesen, während ein unbeschrifteter Baum, der manchmal auch als Baumform bezeichnet wird, nur eine Topologie definiert. Einige sequenzbasierte Bäume, die aus einem kleinen genomischen Locus erstellt wurden, wie Phylotree, weisen interne Knoten auf, die mit abgeleiteten Vorfahren-Haplotypen markiert sind.
Aufzählen von Bäumen

Die Anzahl möglicher Bäume für eine gegebene Anzahl von Blattknoten hängt vom spezifischen Baumtyp ab, aber es gibt immer mehr beschriftete als nicht beschriftete Bäume, mehr verzweigte als sich gabelnde Bäume und mehr verwurzelte als unbewurzelte Bäume. Die letzte Unterscheidung ist die biologisch relevanteste; es entsteht, weil es viele Stellen auf einem unbewurzelten Baum gibt, um die Wurzel zu setzen. Bei gegabelten markierten Bäumen beträgt die Gesamtzahl der verwurzelten Bäume:
- for steht für die Anzahl der Blattknoten.
Bei gegabelten markierten Bäumen beträgt die Gesamtzahl der unbewurzelten Bäume:
- für .
Unter den gekennzeichneten gabelförmigen Bäumen ist die Anzahl der unbewurzelten Bäume mit Blättern gleich der Anzahl der bewurzelten Bäume mit Blättern.
Die Anzahl der bewurzelten Bäume wächst schnell in Abhängigkeit von der Anzahl der Spitzen. Für 10 Spitzen gibt es mehr als mögliche sich gabelnde Bäume, und die Zahl der sich gabelnden Bäume steigt mit ca. Siebenmal so viele der letzteren wie die ersteren.
| Beschriftete Blätter |
Binäre unbewurzelte Bäume |
Binär verwurzelte Bäume |
Multifurcating verwurzelte Bäume |
Alle möglichen verwurzelten Bäume |
|---|---|---|---|---|
| 1 | 1 | 1 | 0 | 1 |
| 2 | 1 | 1 | 0 | 1 |
| 3 | 1 | 3 | 1 | 4 |
| 4 | 3 | fünfzehn | 11 | 26 |
| 5 | fünfzehn | 105 | 131 | 236 |
| 6 | 105 | 945 | 1.807 | 2.752 |
| 7 | 945 | 10,395 | 28.813 | 39.208 |
| 8 | 10,395 | 135.135 | 524.897 | 660.032 |
| 9 | 135.135 | 2.027.025 | 10.791.887 | 12.818.912 |
| 10 | 2.027.025 | 34.459.425 | 247.678.399 | 282.137.824 |
Besondere Baumarten
Dendrogramm
Ein Dendrogramm ist eine allgemeine Bezeichnung für einen Baum, ob phylogenetisch oder nicht, und damit auch für die schematische Darstellung eines phylogenetischen Baumes.
Kladogramm
Ein Kladogramm stellt nur ein Verzweigungsmuster dar; dh seine Zweiglängen repräsentieren nicht die Zeit oder den relativen Betrag der Zeichenänderung, und seine internen Knoten repräsentieren keine Vorfahren.

Phylogramm
Ein Phylogramm ist ein phylogenetischer Baum, dessen Zweiglängen proportional zum Ausmaß der Charakteränderung sind.
Ein Chronogramm ist ein phylogenetischer Baum, der die Zeit explizit durch seine Zweiglängen repräsentiert.
Dahlgrenogramm
Ein Dahlgrenogramm ist ein Diagramm, das einen Querschnitt eines phylogenetischen Baumes darstellt
Phylogenetisches Netzwerk
Ein phylogenetisches Netzwerk ist streng genommen kein Baum, sondern ein allgemeinerer Graph oder im Fall von Wurzelnetzwerken ein gerichteter azyklischer Graph . Sie werden verwendet, um einige der Einschränkungen zu überwinden , die Bäumen inhärent sind.
Spindeldiagramm

Ein Spindeldiagramm oder Blasendiagramm wird nach seiner Popularisierung durch den amerikanischen Paläontologen Alfred Romer oft als Romerogramm bezeichnet . Es stellt die taxonomische Vielfalt (horizontale Breite) gegen die geologische Zeit (vertikale Achse) dar, um die Variation der Häufigkeit verschiedener Taxa im Laufe der Zeit widerzuspiegeln. Ein Spindeldiagramm ist jedoch kein evolutionärer Baum: Die taxonomischen Spindeln verschleiern die tatsächlichen Beziehungen des Elterntaxons zum Tochtertaxon und haben den Nachteil, dass sie die Paraphylie der Elterngruppe mit einbeziehen . Diese Art von Diagramm wird in der ursprünglich vorgeschlagenen Form nicht mehr verwendet.
Korallen des Lebens
Darwin erwähnte auch, dass die Koralle eine geeignetere Metapher als der Baum sein könnte . Tatsächlich sind phylogenetische Korallen nützlich, um vergangenes und gegenwärtiges Leben darzustellen, und sie haben einige Vorteile gegenüber Bäumen (Anastomosen erlaubt usw.).
Konstruktion
Phylogenetische Bäume, die mit einer nicht trivialen Anzahl von Eingabesequenzen zusammengesetzt sind, werden unter Verwendung von Methoden der computergestützten Phylogenetik konstruiert . Distanz-Matrix-Methoden wie Neighbor-Joining oder UPGMA , die die genetische Distanz aus mehreren Sequenz-Alignments berechnen , sind am einfachsten zu implementieren, berufen sich jedoch nicht auf ein evolutionäres Modell. Viele Sequenz-Alignment-Methoden wie ClustalW erzeugen auch Bäume, indem sie die einfacheren Algorithmen (dh die auf Distanz basierenden) der Baumkonstruktion verwenden. Maximale Sparsamkeit ist eine weitere einfache Methode zur Schätzung phylogenetischer Bäume, impliziert jedoch ein implizites Evolutionsmodell (dh Sparsamkeit). Fortgeschrittenere Methoden verwenden das Optimalitätskriterium der maximalen Wahrscheinlichkeit , oft innerhalb eines Bayesschen Rahmens , und wenden ein explizites Evolutionsmodell auf die phylogenetische Baumschätzung an. Das Identifizieren des optimalen Baums unter Verwendung vieler dieser Techniken ist NP-schwer , daher werden heuristische Such- und Optimierungsverfahren in Kombination mit Baumbewertungsfunktionen verwendet, um einen angemessen guten Baum zu identifizieren, der zu den Daten passt.
Baumbaumethoden können anhand mehrerer Kriterien beurteilt werden:
- Effizienz (wie lange dauert die Berechnung der Antwort, wie viel Speicher wird benötigt?)
- Macht (nutzt es die Daten gut oder werden Informationen verschwendet?)
- Konsistenz (wird es wiederholt auf dieselbe Antwort konvergieren, wenn jedes Mal unterschiedliche Daten für dasselbe Modellproblem gegeben werden?)
- Robustheit (Kommt es gut mit Verletzungen der Annahmen des zugrunde liegenden Modells zurecht?)
- Falsifizierbarkeit (warnt es uns, wenn es nicht gut zu verwenden ist, dh wenn Annahmen verletzt werden?)
Baumbautechniken haben auch die Aufmerksamkeit von Mathematikern auf sich gezogen. Bäume können auch mit der T-Theorie erstellt werden .
Dateiformate
Bäume können in einer Reihe verschiedener Formate codiert werden, die alle die verschachtelte Struktur eines Baums darstellen müssen. Sie können Verzweigungslängen und andere Merkmale codieren oder nicht. Standardisierte Formate sind entscheidend für die Verteilung und gemeinsame Nutzung von Bäumen, ohne auf Grafikausgaben angewiesen zu sein, die sich nur schwer in vorhandene Software importieren lassen. Häufig verwendete Formate sind
Grenzen der phylogenetischen Analyse
Obwohl phylogenetische Bäume, die auf der Grundlage von sequenzierten Genen oder genomischen Daten in verschiedenen Arten erstellt wurden, evolutionäre Erkenntnisse liefern können, haben diese Analysen wichtige Einschränkungen. Am wichtigsten ist, dass die Bäume, die sie erzeugen, nicht unbedingt korrekt sind – sie geben die Evolutionsgeschichte der enthaltenen Taxa nicht unbedingt genau wieder. Wie jedes wissenschaftliche Ergebnis unterliegen sie der Fälschung durch weitere Studien (zB Erhebung zusätzlicher Daten, Analyse der vorhandenen Daten mit verbesserten Methoden). Die Daten, auf denen sie basieren, können verrauscht sein ; die Analyse kann durch genetische Rekombination , horizontalen Gentransfer , Hybridisierung zwischen Arten , die vor der Hybridisierung nicht nächste Nachbarn auf dem Baum waren , konvergente Evolution und konservierte Sequenzen verwechselt werden .
Außerdem gibt es Probleme, eine Analyse auf einen einzelnen Charaktertyp, wie ein einzelnes Gen oder Protein, oder nur auf eine morphologische Analyse zu stützen , da solche Bäume, die aus einer anderen, nicht verwandten Datenquelle erstellt wurden, sich oft von der ersten unterscheiden und daher große Sorgfalt erforderlich ist bei der Ableitung phylogenetischer Beziehungen zwischen den Arten. Dies trifft am meisten auf genetisches Material zu, das einem lateralen Gentransfer und einer Rekombination unterliegt , wobei verschiedene Haplotypblöcke unterschiedliche Geschichten haben können. Bei diesen Analysearten ist der Ausgabebaum einer phylogenetischen Analyse eines einzelnen Gens jedoch eine Schätzung der Phylogenie des Gens (dh eines Genbaums) und nicht der Phylogenie der Taxa (dh Artenbaum), aus denen diese Merkmale entnommen wurden idealerweise sollten beide sehr nahe beieinander liegen. Aus diesem Grund ernsthafte phylogenetische Studien im Allgemeinen eine Kombination von Genen verwendet werden, die aus verschiedenen genomischen Quellen stammen (zB von mitochondrialen oder Plastiden gegen Atom Genome) oder Gene , die unter verschiedenen selektiven Regime zu entwickeln wäre zu erwarten, so dass Homoplasie (false Homologie ) ist unwahrscheinlich, dass sie aus natürlicher Selektion resultieren.
Wenn ausgestorbene Arten als Endknoten in eine Analyse einbezogen werden (anstatt beispielsweise interne Knoten einzuschränken), werden sie nicht als direkte Vorfahren einer vorhandenen Art angesehen. Ausgestorbene Arten enthalten normalerweise keine hochwertige DNA .
Die Palette nützlicher DNA-Materialien hat sich mit Fortschritten in den Extraktions- und Sequenzierungstechnologien erweitert. Die Entwicklung von Technologien, die in der Lage sind, Sequenzen aus kleineren Fragmenten oder aus räumlichen Mustern von DNA-Abbauprodukten abzuleiten, würde den als nützlich erachteten DNA-Bereich weiter erweitern.
Phylogenetische Bäume können auch aus einer Reihe anderer Datentypen abgeleitet werden, darunter Morphologie, das Vorhandensein oder Fehlen bestimmter Gentypen, Insertions- und Deletionsereignisse – und jede andere Beobachtung, von der angenommen wird, dass sie ein evolutionäres Signal enthält.
Phylogenetische Netzwerke werden verwendet, wenn sich gabelnde Bäume aufgrund dieser Komplikationen nicht eignen, die auf eine stärker vernetzte Evolutionsgeschichte der beprobten Organismen hindeuten.
Siehe auch
Verweise
Weiterlesen
- Schuh, RT und AVZ Brower. 2009. Biologische Systematik: Prinzipien und Anwendungen (2. Aufl.) ISBN 978-0-8014-4799-0
- Manuel Lima , The Book of Trees: Visualizing Branches of Knowledge , 2014, Princeton Architectural Press, New York.
- MEGA , eine kostenlose Software zum Zeichnen phylogenetischer Bäume.
- Gontier, N. 2011. "Darstellung des Lebensbaums: die philosophischen und historischen Wurzeln evolutionärer Baumdiagramme." Evolution, Bildung, Öffentlichkeitsarbeit 4: 515–538.
Externe Links
Bilder
- Humanes Y-Chromosom 2002 Phylogenetischer Baum
- iTOL: Interaktiver Lebensbaum
- Phylogenetischer Stammbaum künstlicher Organismen, die auf Computern entwickelt wurden
- Miyamoto und Goodmans Phylogramm der Eutherischen Säugetiere
Allgemein
- Eine Übersicht über verschiedene Methoden der Baumvisualisierung findet sich bei Page, RDM (2011). „Raum, Zeit, Form: Den Baum des Lebens betrachten“. Trends in Ökologie und Evolution . 27 (2): 113–120. doi : 10.1016/j.tree.2011.12.002 . PMID 22209094 .
- OneZoom: Tree of Life – alle lebenden Arten als intuitiver und zoombarer Fraktal-Explorer (Responsive Design)
- Discover Life Ein interaktiver Baum, der auf dem Projekt Assembling the Tree of Life der US National Science Foundation basiert
- PhyloCode
- Ein multiples Alignment von 139 Myosinsequenzen und ein phylogenetischer Baum
- Baum des Lebens Webprojekt
- Phylogenetische Schlussfolgerungen auf dem T-REX-Server
- Taxonomie-Datenbank des NCBI [1]
- ETE: A Python Environment for Tree Exploration Dies ist eine Programmierbibliothek zum Analysieren, Manipulieren und Visualisieren phylogenetischer Bäume. Art.-Nr.
- Ein täglich aktualisierter Baum des (sequenzierten) Lebens Fang, H.; Hafer, ME; Pethica, RB; Greenwood, JM; Sardar, AJ; Rackham, OJL; Donoghue, PCJ; Stamatakis, A.; De Lima Morais, DA; Gough, J. (2013). „Ein täglich aktualisierter Baum des (sequenzierten) Lebens als Referenz für die Genomforschung“ . Wissenschaftliche Berichte . 3 : 2015. Bibcode : 2013NatSR...3E2015F . doi : 10.1038/srep02015 . PMC 6504836 . PMID 23778980 .










